Hello Virtul Cell
Virtual Cell 研究计划的最小可执行 Demo 用最少的代码贯通"研究计划"中四个阶段的完整流程: 数据 → 表征 → 扰动预测 → 机理耦合 → 可视化。
本 MVP 不追求 SOTA,而是给出一条可一键运行的 pipeline 骨架,所有代码 < 1500 行, CPU + 8GB 内存即可跑通(不需要 GPU、不需要下载海量数据)。后续每个模块都可以 被替换成真正的 SOTA 模型(scGPT / GEARS / CellOT / cobrapy 等)而不破坏整体框架。
点击图片跳转视频 → 使用 CELLxGENE Census 真实血液 T 细胞数据跑通 4 阶段 pipeline,并在 Streamlit 中展示各阶段模型推理过程的可视化。
# 1) 进入项目
cd /Users/mac/code/HelloVirtulCell
# 2) 创建虚拟环境并安装依赖(约 2 分钟)
make setup
# 3) 跑通完整流程(约 1-3 分钟)
make all
# 4) 启动交互式虚拟细胞 Demo(浏览器自动打开)
make app或者不用 make:
python -m venv .venv && source .venv/bin/activate
pip install -r requirements.txt
python -m openvcell.pipeline # 跑完 4 阶段
streamlit run openvcell/app.py # 启动 demoHelloVirtulCell/
├── research_plan.md # 完整研究计划 (上一步生成)
├── README.md # 本文件
├── requirements.txt
├── Makefile
├── openvcell/
│ ├── __init__.py
│ ├── config.py # 全局配置
│ ├── stage1_data.py # Stage 1: 数据底座 (合成 / 真实数据加载)
│ ├── stage2_foundation.py # Stage 2: 单细胞基础模型 (mini-Transformer)
│ ├── stage3_perturb.py # Stage 3: 扰动响应预测 (CPA-lite)
│ ├── stage4_mechanism.py # Stage 4: 机理耦合 (toy FBA + 通路一致性)
│ ├── evaluate.py # 评估指标
│ ├── pipeline.py # 串联所有阶段的入口
│ └── app.py # Streamlit 交互 demo
├── tests/
│ └── test_pipeline.py # 烟雾测试
└── artifacts/ # 自动生成: 数据、模型、图表
| 阶段 | 模块 | 做了什么(MVP 实现) | 真实研究里替换为 |
|---|---|---|---|
| Stage 1 | stage1_data.py |
生成 / 加载 AnnData:2000 cells × 200 genes,含 3 种 cell type、5 种扰动;自动 QC + log-normalize |
CELLxGENE Census / scPerturb |
| Stage 2 | stage2_foundation.py |
一个 4 层 Transformer encoder,对 (gene, expr) 序列做 masked-expression 重建,输出 cell embedding | scGPT / Geneformer / UCE |
| Stage 3 | stage3_perturb.py |
CPA-lite:cell embedding + 扰动 one-hot → MLP → ΔExpression;leave-perturb-out 评估 | CPA / GEARS / CellOT / Flow Matching |
| Stage 4 | stage4_mechanism.py |
Toy FBA:把预测表达映射到酶丰度,用 scipy.optimize.linprog 求最大生物量通量;与 KEGG-style 通路 prior 算一致性 |
cobrapy + Human-GEM + tellurium |
| 评估 | evaluate.py |
Pearson Δ、Top-K DEG 召回、cell-type macro-F1、通路一致性 | Open Problems / PerturBench / scIB |
| Demo | app.py |
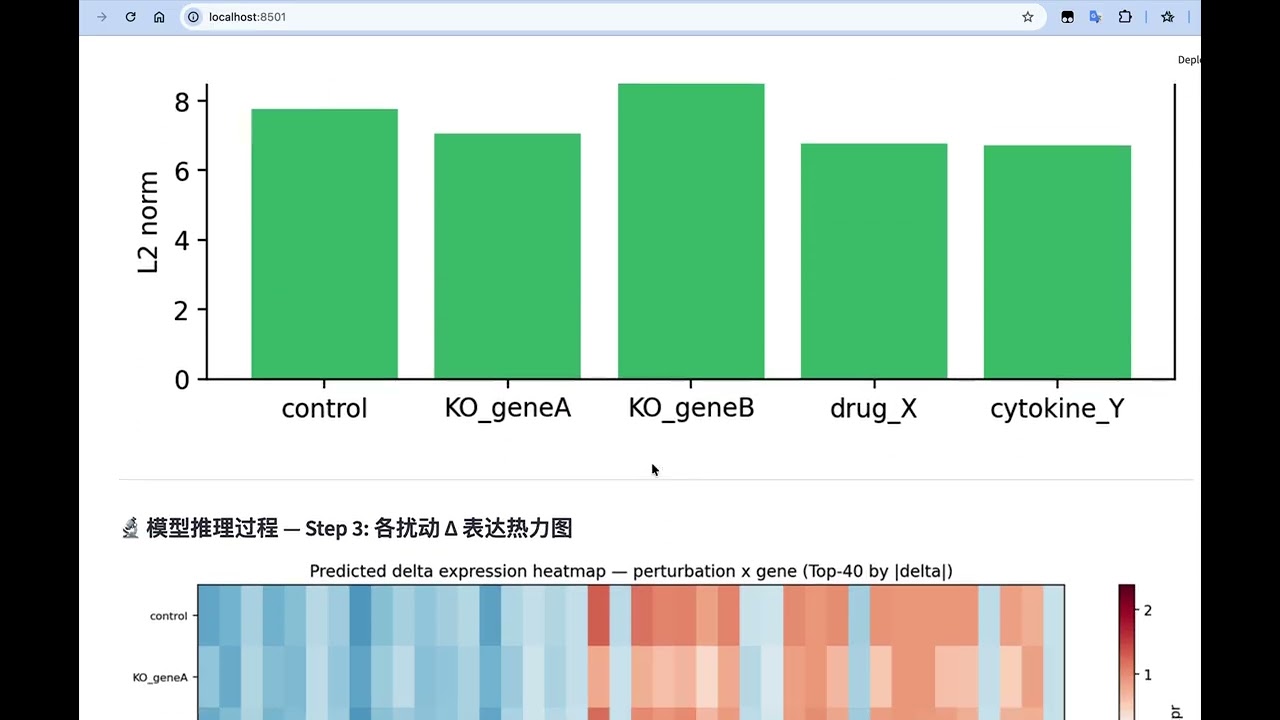
Streamlit:选 cell type + 扰动 → 输出预测表达、UMAP、代谢通量、通路富集 | 同款,可换真模型 |
默认使用合成数据,方便首次跑通。要切换到真实数据,把 config.py 中:
USE_REAL_DATA = False改为 True 后,stage1_data.py 会用 cellxgene-census 拉取 ~5k 真实人 PBMC 单细胞
(约 50MB,需联网),其余阶段无需改动。
跑完 make all 后,artifacts/report.md 会包含:
- 数据 QC 指标
- 基础模型重建 loss 曲线
- 扰动预测 Pearson / Top-20 DEG recall
- 代谢通量预测 vs ground truth 的 R²
- UMAP 可视化(对照 vs 扰动)
research_plan.md ──► 本 MVP 的可执行版本
Stage 1 数据底座 ──► openvcell/stage1_data.py
Stage 2 基础模型 ──► openvcell/stage2_foundation.py
Stage 3 扰动预测 ──► openvcell/stage3_perturb.py
Stage 4 多尺度耦合 ──► openvcell/stage4_mechanism.py
评估基准 ──► openvcell/evaluate.py
交互 demo ──► openvcell/app.py
每个文件顶部都有 # TODO: replace with <真实工具> 注释,标明在真实研究中应该替换成哪个 SOTA。
- 把
stage1_data.py替换为cellxgene-census+scvi-tools真实流水线。 - 把
stage2_foundation.py升级为 scGPT/Geneformer 官方权重 + LoRA 微调。 - 把
stage3_perturb.py升级为 GEARS 或自研 Flow Matching。 - 把
stage4_mechanism.py接入cobrapy+ Human-GEM。 - 加入 Cell Painting 形态分支(
cellprofiler特征 → CLIP 对齐)。
这就是把"hello world"的虚拟细胞,逐步演化成真正 OpenVCell-v0.1 的路径。